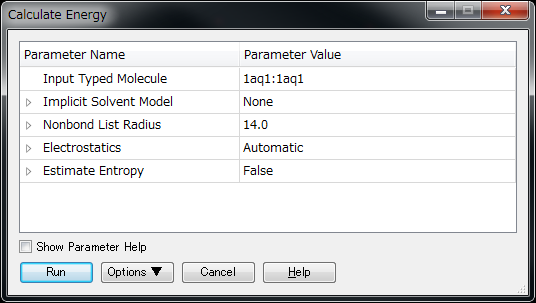
1. はじめに¶
本書は、Discovery Studioを東京工業大学学術国際情報センターのTSUBAMEで利用する方法について説明しています。
また、TSUBAMEを利用するにあたっては、TSUBAME3.0利用の手引きもご覧下さい。
利用環境や注意事項などが詳細に記述されております。
ダッソー・システムズ・バイオビア株式会社ではDiscovery Studioに関するWebページを公開しています。
下記のアドレスを参照してください。
1.1. 利用できるバージョン¶
TSUBAME3で利用可能な最新バージョンについてはTSUBAME計算サービスWebサイトの アプリケーション ページをご確認下さい。
研究に支障がない限り、バグ修正の入っている最新版をご利用下さい。
1.2. 利用環境及び入手方法¶
Discovery Studioはクライアント‐サーバー方式のソフトウェアです。 本学ではWindows版のDiscovery Studioを学内配布しております。 ご利用を希望される場合は、所定の手続きに従って申請を行い、インストーラーと共に提供される手順書に従ってインストールを行ってください。
1.3. 概要¶
Discovery Studioはライフサイエンス研究向けのモデリング・シミュレーション環境です。データの取得から分析までを担う一連の製品で構成されています。
共通の基盤技術とデータモデルを使用することで、研究で使用されるあらゆる方法論をシームレスに組み合わせて、さまざまな計算上の問題を解決することができます。
Discovery Studioに含まれるモジュールは以下の通りです。
DS Modeling Visualizer Pro
- 3次元構造、ファイルの可視化、3次元構造においての原子・分子の編集が可能
- シーケンスウィンドウでマルチプルアライメントを表示
- シーケンスウィンドウと3次元構造ウィンドウが相互に反映
DS Biopolymer
- ポリペプチドのシーケンスをウィザードから入力(選択)することで、ペプチド構築、編集が可能
- タンパク質やリガンドなどを同一ウィンドウ、あるいは別々のウィンドウで同時に表示可能。 タンパク質等の構造エラーを自動的に修正
DS CHARMm(分子力学・動力学計算モジュール)
- 低分子から生体高分子に最適化された力場パラメーターを備えており、豊富な実績を持つ、 高度に認められ広く使われるシミュレーションパッケージ
DS Analysis
- DS CHARMmモジュールを使用して、計算した結果の解析及びアニメーション化
DS MODELER
- 自動的にタンパク質をホモロジーモデリング
- ウィザードの使用で簡単にループ修正
- シーケンスアライメント(2D、3D)が実行可能
- 拘束定義(Cis-prolines、disulphide bonds)、 アライメントの作成(シーケンスのidentity/similarity値を表示)
DS Protein Similarity Search
- タンパク質シーケンスのホモロジーを識別
- Web、ローカルのデータベースより検索(BLAST、gapped-BLAST、PSI-BLAST)、 ソートテーブル、ヒットテーブル、アラインシーケンスを自動的に作成
DS CFF
- 生体高分子及び低分子のためのCHARMmの力場オプション
DS Delphi
- Poisson-Boltzmann関数を使用した静電荷及び溶媒和計算
- 3次元静電荷エネルギー表示(グリッド、体積、固体)、 Delphiでの静電荷ポテンシャルに基づいて色で表示
DS Protein Families
- 進化系統樹を用いてタンパク質の機能に重要な残基を解析
- マルチプルシーケンスアライメント
- Aline123法(ClustalWを改良)
- Pre-alignedプロファイルの選択可
- シーケンスの進化関係、conservationパターンを元にファミリータンパク質を解析。 側鎖距離と露出残基によって残基をクラスター化
DS Protein Health
- Profiles-3Dを使用して、タンパク質構造を評価
- タンパク質全体、あるいは残基単位での計算が可能
DS LigandFit
- タンパク質-リガンドの親和性評価を高速/高精度に実行
- Cavity検索による活性部位探索
- 高速モンテカルロによるコンフォメーション空間の検索
- エネルギーグリッド計算を用いたドッキング配置/配座の高速な評価
DS LigScore
- 独自スコアリング関数LigScore2を含む各種スコアリング関数で タンパク-リガンドの結合親和性をスコア評価
DS Ludi
- タンパク構造既知、ターゲットリガンド構造未知の場合のリガンドのde novoデザイン。 タンパク質の結合部位に立体的化学的に適合
- リガンド-タンパク質複合体のスコアリング
- 結合親和性を増加させるような既知リガンド改変の示唆
1.4. マニュアル¶
Windows版 Discovery Studioにヘルプがあります。
Discovery Studio起動後にメニューバーの「Help」→「Help Topics」を選択するとブラウザが起動し、ヘルプ画面が表示されます。
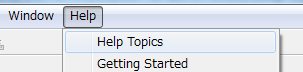
または、マウスポインタを項目上に置くと、その項目の簡単な説明が表示されます。
その説明の下部の「Click here for help」をクリックするとその項目に関するヘルプ画面が表示されます。
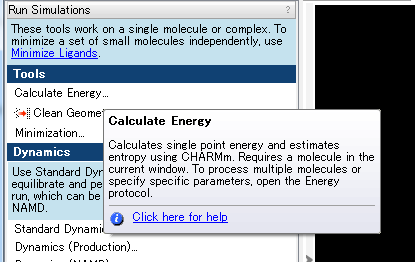
ダイアログの「Help」をクリックすることでもヘルプ画面を表示することができます。