5. プロトコル実行例¶
5.1. タンパク質の構造最適化計算¶
この節では、RCSB PDBから取得した1crnの構造最適化を行います。
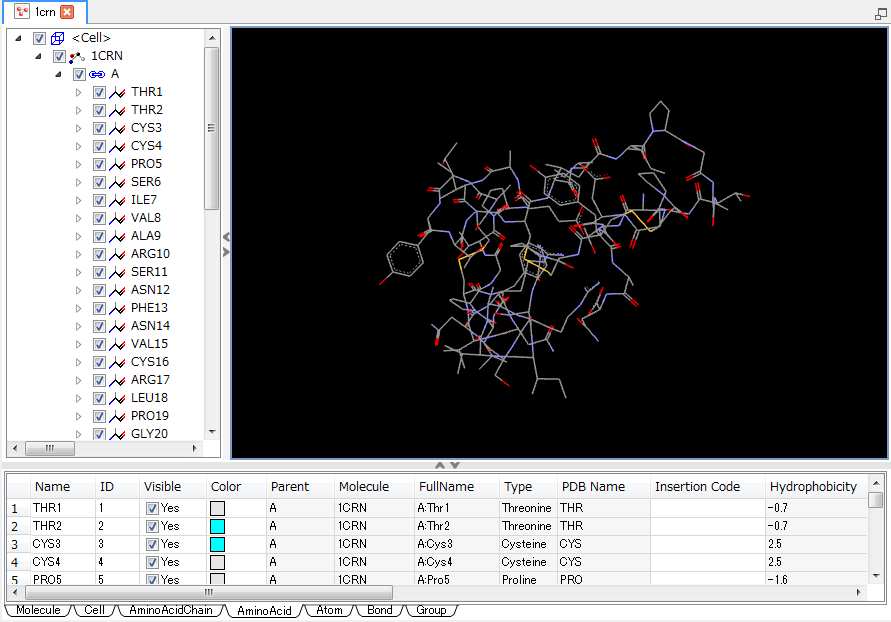
まず、1crnを開きます。
Display StyleをLineに変更します
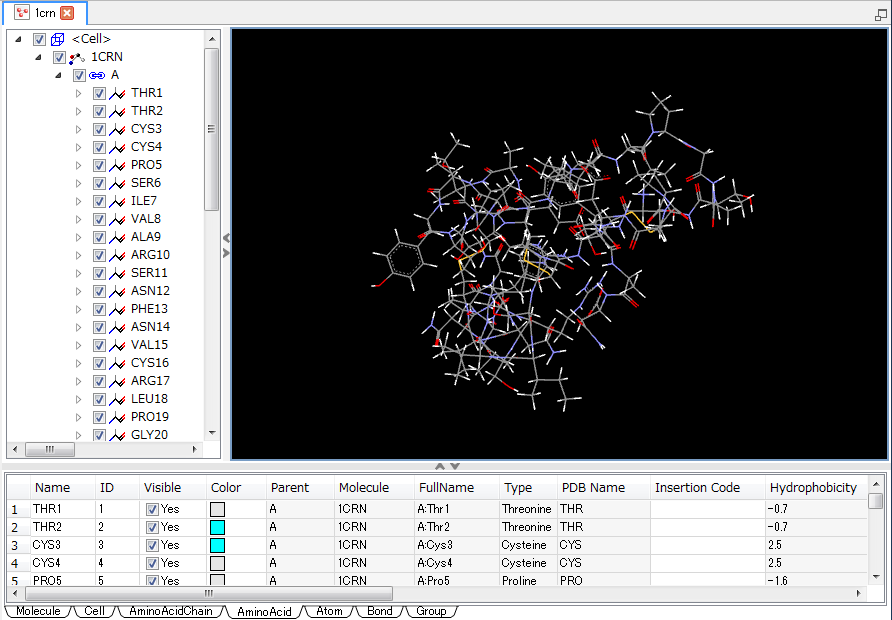
Add hydrogen ボタンをクリックして、水素を付加します。
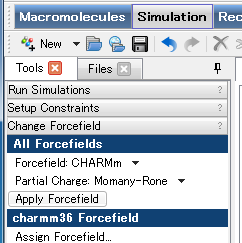
次に力場と電荷のタイプを設定します。
「Simulation」Tool Setを選択し、「Tools」Explorerの「Change Forcefield」をクリックして展開します。
Forcefield 及びPartial Chargeを設定します。
この例では、Forcefield にCHARMmを、Partial ChargeにMomany-Roneを選択します。
選択したら、Apply Forcefieldをクリックして適用します。
次に、Tools ExplorerのRun Simulationsを展開し、Tools > Minimization をクリックし、Minimizationダイアログを開きます。
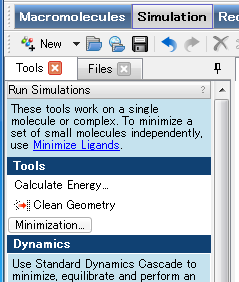
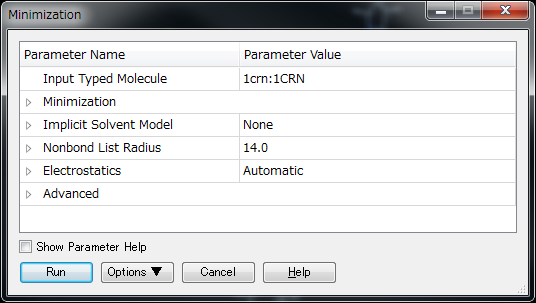
各パラメーターの詳細は、Helpをご参照ください。
この例では、デフォルトのままRunをクリックします。
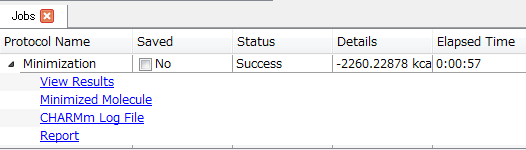
計算が開始され、以下のウィンドウが表示されます。
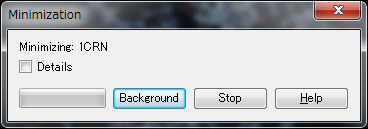
進捗はJobs Explorerで確認できます。
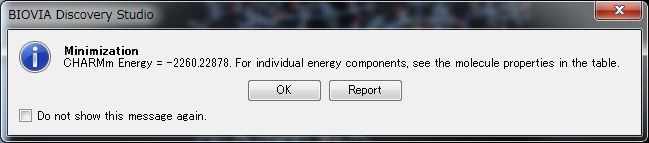
計算が完了すると以下のように表示されますので、OKをクリックします。
5.2. 計算結果の確認¶
計算を実行している間、結果は、Set as defaultで指定したフォルダーに、”プロトコル名_年月日_時間” というフォルダー名で作成されます。
作成されたフォルダーのOutputフォルダーに計算結果ファイルが作成されます。
出力結果は、使用したプロトコルにより変わります。
この例では、下表に示すファイルが作成されます。
| ファイル名 | 内容 |
|---|---|
| charmm.log | CHARMMによる計算結果 |
| 1CRN.mol2 | Minimizationによって得られた構造ファイル |
| Output.log | 計算サーバからのコマンドとその返答の内容を保存したファイル エラー終了した場合、本ファイルを参照し、問題点を見出してください |
| Report.htm | 計算結果を纏めたHTML形式のファイル |
計算結果は、Jobs Explorerから呼び出すことも可能です。